|
原创世界: 【Dragicland】 头衔: 记录世界的探险家
|
| ||||
|
原创世界: 【烈火流星】 头衔: 姊姊的妹妹(?)
|
| ||||
|
原创世界: 【Dragicland】 头衔: 记录世界的探险家
|
| ||||
|
|
|
|
「你到底是誰?」巨狼芬利斯咆哮著問道。
「你知道我是約書亞,」一直以來化身為小孩的救主逐漸消失在光中,他的聲音仍在空氣中迴盪,「不管我是誰,我是你和伊利諾的朋友,這點永不改變。」 ——賓根的約翰,耶穌與伊利諾人之祖芬利斯的對話,《伊利諾村的起源故事》,主後十二世紀。 |
|
|
原创世界: 【Dragicland】 头衔: 记录世界的探险家
|
| ||||

















 发表于 2013-9-27 20:52
|
发表于 2013-9-27 20:52
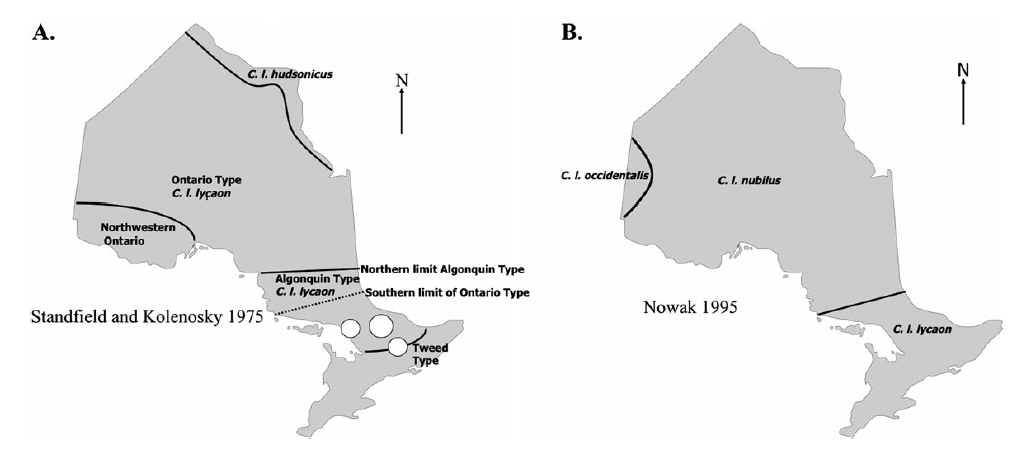
| 
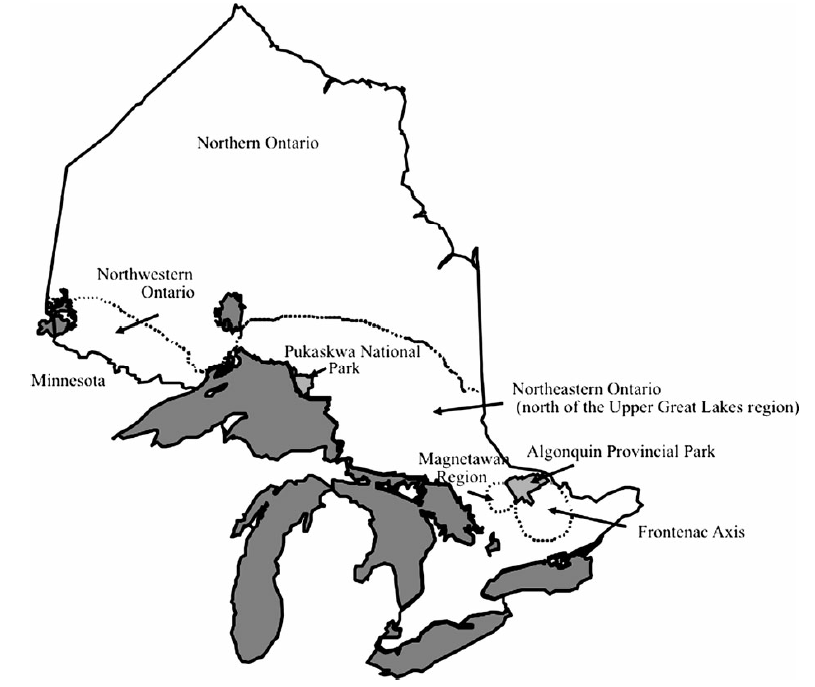
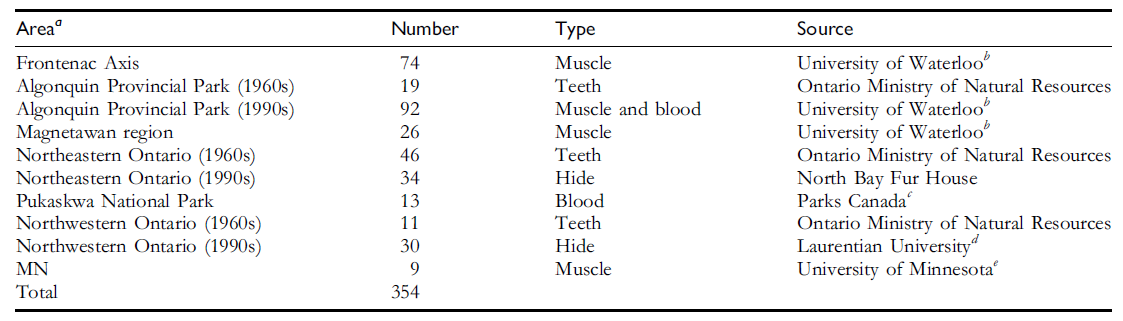
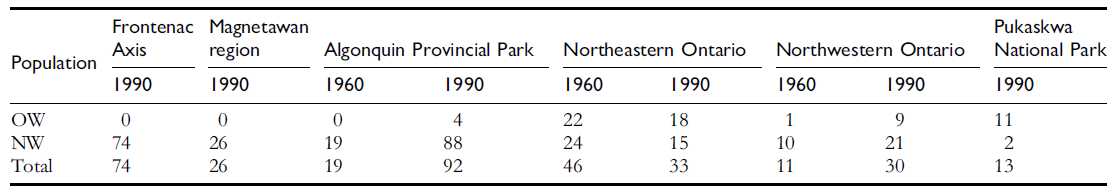
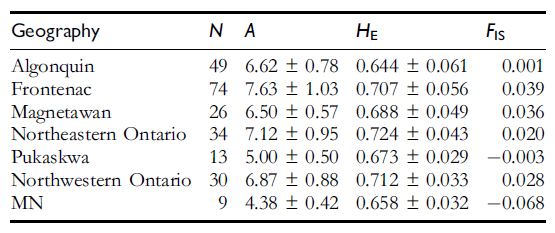

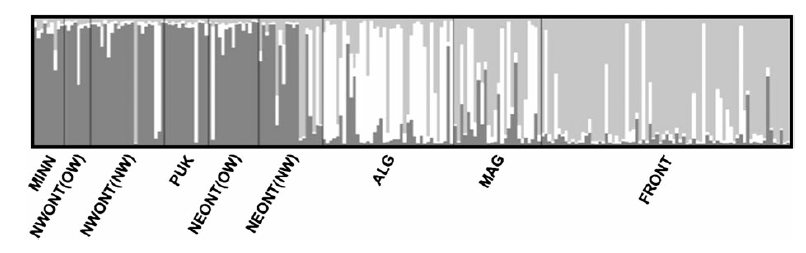
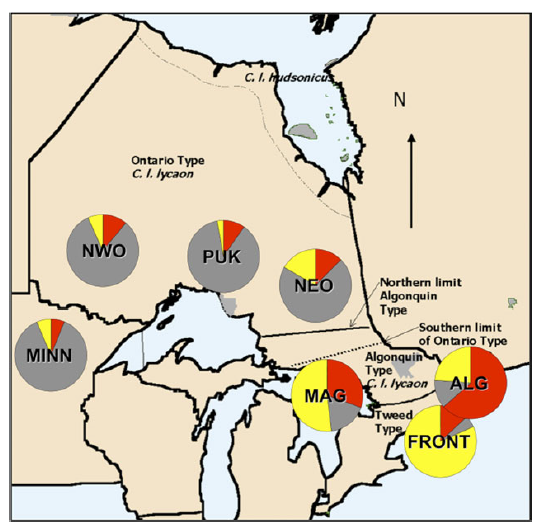
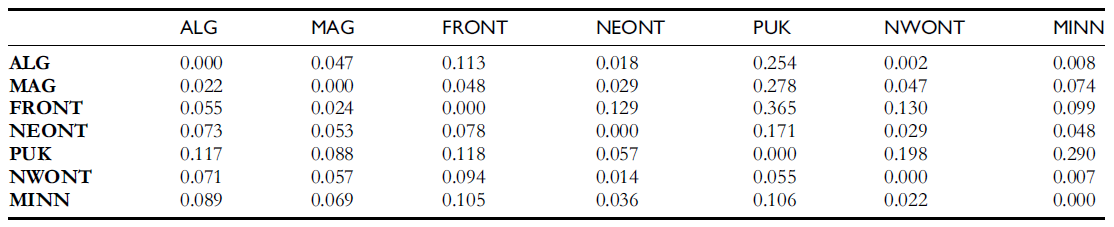






 发表于 2013-10-1 18:50
|
发表于 2013-10-1 18:50
| 







 发表于 2013-10-19 08:04
|
发表于 2013-10-19 08:04
| 