|
  
原创世界: 【Dragicland】
头衔: 记录世界的探险家
- 帖子
- 6840
- 主题
- 1374
- 探险经验
- 31405
- 卡币
- 15465 F
- 头像出处
- 一只萌灿
|
原文在此:http://www.sciencemag.org/content/342/6160/871.abstract
Complete Mitochondrial Genomes of Ancient Canids Suggest a European Origin of Domestic Dogs
对史前犬科动物的全线粒体基因组分析显示家犬起源于欧洲
O. Thalmann, B. Shapiro, P. Cui, V. J. Schuenemann, S. K. Sawyer, D. L. Greenfield, . B. Germonpré, M. V. Sablin, F. López-Giráldez, X. Domingo-Roura, H. Napierala, H-P. Uerpmann, D. M. Loponte, A. A. Acosta, L. Giemsch, R. W. Schmitz, B. Worthington, J. E. Buikstra, A. Druzhkova, A. S. Graphodatsky, N. D. Ovodov, N. Wahlberg, A. H. Freedman, R. M. Schweizer, K.-P. Koepfli, J. A. Leonard, M. Meyer, J. Krause, S. Pääbo, R. E. Green, R. K. Wayne
家犬起源于何时何地在当今仍是一个备受争论的话题,基因数据表明驯化开始于15,000年前的东亚,而在欧洲和西伯利亚人们发掘出了历史超过30,000年的似犬动物的化石。我们分析了18只来自欧亚大陆和新大陆的史前犬科动物,并将其与现代的狗和狼进行比较。现代狗的线粒体基因从系统发育上看和史前或现代的欧洲犬科动物更加相近。分子方面的数据显示驯化起源于18,800至32,100年前的欧洲。这些发现暗示家犬可能起源于远古欧洲的狩猎-采集文化和犬科动物的接触与相互影响。
狗,是有关驯化和人工选择影响物种进化方面最著名的案例 (1)。驯化通常会造成表型变异,而且这些动物的地理分布也会受到人类扩张的极大影响。因为狗的表型变异实在是太多样了,所以通过比较各犬种之间或狗与其祖先灰狼Canis lupus的特征差异来推断狗的起源,就非常困难了 (2–4)。此外,长久以来不同犬种因为人类的交易而不断地相互杂交、或者和当地的狼杂交、甚至包括一些品系内严重的近亲繁殖以及不完善品系的随机效应,也影响着对遗传信息的分析和推断。尽管如此,人们依然从遗传信息中推断出了狗的起源地,包括中东和东亚 (5–7)。然而,人们却在西欧和西伯利亚发现了距今15,000至36,000年、最古老的狗类遗骨 (2, 8),不过这些样本的分类仍然备受争议 (9)。在中东和东亚发现的狗类遗骨则都是13,000年以内的。
从最早的狗样本中提取的DNA分析显示 (2, 8, 11–14),驯化的表型证据可以用于检验有关现代狗起源的假说。我们通过高通量测序进行DNA捕获 (15),取得了18只史前犬科动物和20只现代欧洲和美洲狼的线粒体基因组序列(表1)。这些样本的DNA片段和预期的先祖DNA相似,包括序列长度和样本年代,以及史前DNA的脱氨基作用模式 (15)。在覆盖长度小于50%的线粒体基因组的过滤、迭代配对和排除后,我们得到了平均12倍(1.9 ~ 625.7)的18个史前基因组覆盖率,其中平均15,014(8667 ~ 16,415)核苷酸覆盖率至少两倍。我们随后再把这些史前犬科动物的mtDNA集合和49只狼、77只狗包括存在分类分歧的犬种巴仙吉犬(Basenji)和澳洲野犬(Dingo)、3种近亲发表的中国本土犬种 (7)、4只郊狼的总计148个全线粒体基因组相比较。
我们在对这些线粒体基因组数据的系统发育分析中运用了最大似然(maximum likelihood)、聚合(coalescence)和贝叶斯方法(Bayesian approaches),得出了一个较好的系统进化树(图1)。尽管狼和狗并非交互单系群(reciprocally monophyletic),但所有现代狗和许多狼都从属于这些分支的其中之一(图1)。在这个系统进化树上,狗属于四个分支之一(Dog A ~ D),分支A包括了大部分狗的序列(64%)。三个来自比利时(Belgian)的史前犬科动物的单倍型在进化树上的位置最远。尽管这其中一种,Goyet dog(Belgium 36,000,图1)的头骨形态和狗相似 (2),但它的mtDNA和其他犬科动物有关,显示其是所有现代狗和现代狼的姐妹类群,而非狗的直系祖先。一个比利时样本(Belgium 26,000)的个体非常大 (2),而且在基因和形态上都和更新世晚期分布在高北极冻土的狼非常不同 (16)。不过,三种来自北极冻土的狼(Alaska 28,000,Alaska 21,000和Alaska 20,800,图1)都不属于这个分支,也非其姐妹群。介于其线粒体存在独特性,比利时犬科动物,包括Goyet dog,可能是一种驯化失败并灭绝的狗,或者一种表型特殊的狼。
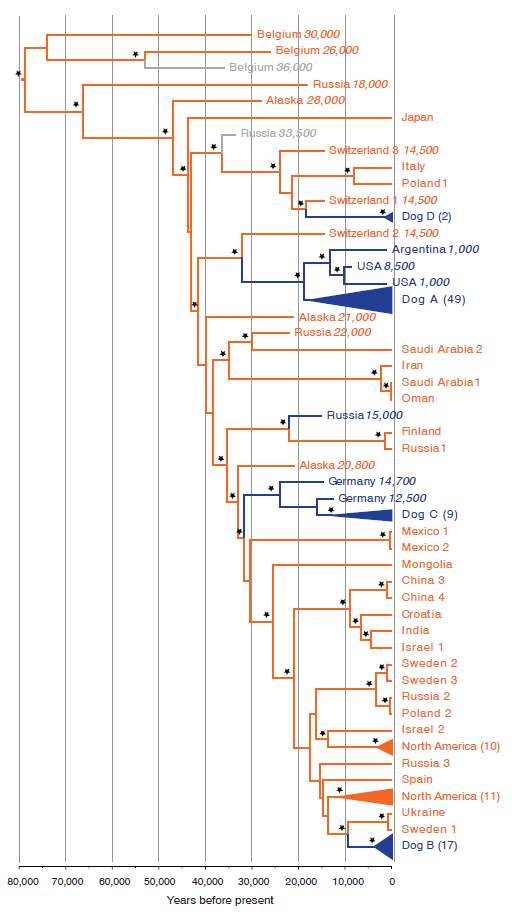
利用聚合、最大似然和贝叶斯方法做出的现代/史前狗(蓝)和狼(橙)的系统进化树。外围的类群(四只郊狼)和两种中国狼序列没有列入其中 (15)。史前样本由出土国家和预测时间标示(斜体的数字代表样本距今的年数)。分类地位不明确的化石样本以灰色标示。若现代犬科动物的序列相似并聚合成一个分支时,我们便用括号标示出各个分支中所包含的序列的数量。星号表示最大似然的自展值(bootstrap values)大于90%,同时贝叶斯分析的后验支持(posterior support)大于0.9。
狗的分支A、C和D涵盖了我们研究中使用的78%的狗序列,而且每一支都是某种或多种史前欧洲犬科动物的姐妹群。其中分支A的变异最多,存在分类分歧的犬种就来源于此,包括巴仙吉犬和澳洲野犬,以及两种中国本土犬类 (7)。此外,三种生活在1000至85000年前、来自新大陆的前哥伦比亚(pre-Colombian)狗,也属于分支A(表1)。分支A的狗和新大陆的狗的最近共同祖先(most recent common ancestor, MRCA)的生活时间为约18,800年前(95%最高后验密度HPD:15,100 ~ 22,600),这意味着新大陆的前哥伦比亚狗和现代狗有着共同的祖先。因此,这些狗可能是和最早的人类一起抵达新大陆的 (17, 18)。这个包含了古老新大陆狗和现代狗的分支A,和在瑞士(Switzerland)Kesslerloch cave出土的古狼(Switzerland 2 14,500)具有距今约32,100年的最近共同祖先(95% HPD:27,500 ~ 36,700)。
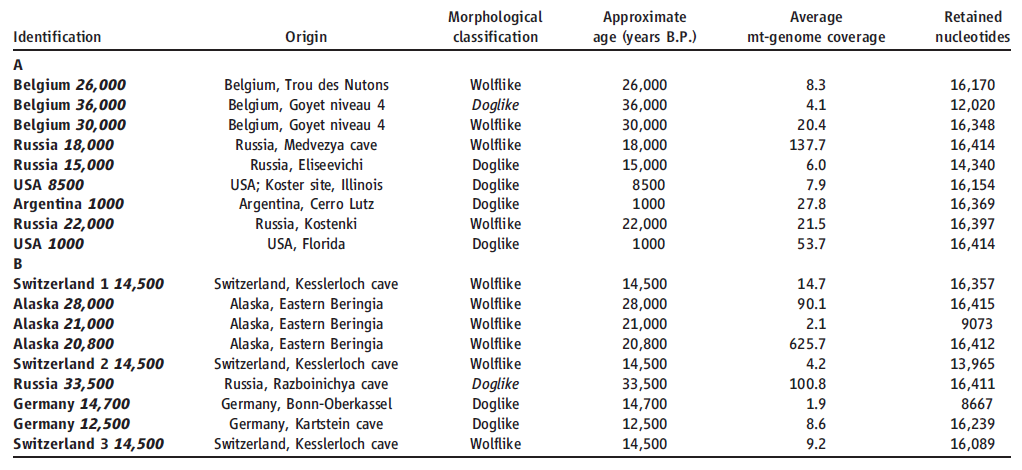
用于实验分析的史前样本。(A) 使用自定义的捕获阵列捕获的史前样本取得数据。(B) 对于含量丰富的mtDNA样本,我们使用长片段PCR扩增和生物素标记 (15) 取得数据。样本的形态分类(morphological classification)和近似年代(approximate age)数据是通过其他的相关资料获得的。样本的形态分类若不明确,则以斜体标示。
分支D是变异最少的支系,只包含两个斯堪的纳维亚(Scandinavian)的犬种,同时和瑞士的一种似狼犬科动物具有距今约18,300年的共同祖先(95% HPD:15,300 ~ 21,900)。这个分支和另一种欧洲史前狼、以及波兰(Poland)和意大利(Italy)的现代狼密切相关,并且起源于俄罗斯(Russia)阿尔泰山脉(Altai Mountains)的假定的早期狗类 (13)。尽管分支D和远古狼与阿尔泰样本存在如此联系,但阿尔泰的狗类并非大部分现代狗的直系祖先。不过,分支D的狗可能和远古狼和早期人类带到斯堪的纳维亚的狗存在杂交 (19),因此影响了其单倍型。
分支C包含了12%的现代狗(9/77),其最近的姐妹类群为两种形态不同、分别来自德国(Germany)Bonn-Oberkassel (12) 和Kartstein cave (14) 的史前狗类(Germany 14,700 和Germany 12,500),MRCA生活在距今16,000至24,000年前(95% HPD:13,500 ~ 28,100)。最后,分支B,涵盖了22%的现代狗(17/77),和瑞典(Sweden)和乌克兰(Ukraine)的现代狼亲缘关系最近,其MRCA生活在距今约9200年前(95% HPD:6500 ~ 12,300)。
分支A、C和D的现代狗和欧洲史前犬科动物的关系、以及分支B的现代狗和欧洲狼的联系,意味着狗起源于欧洲,而非像人们先前认为的那样起源于中东和东亚 (5–7)。严谨地说,没有一个来自中东(沙特阿拉伯Saudi Arabia、阿曼Oman、以色列Israel、伊朗Iran和印度India)或东亚(中国China、日本Japan和蒙古Mongolia)的现代狼的序列和这些现代狗的分支具有近的亲缘关系。对分化时间进行贝叶斯分析的结果显示,家犬起源自18,800至32,100年前的欧洲,上限为分支A的狗和古狼的MRCA时间,下限为多样性最高的狗分支的MRCA时间(图1)。因此,我们的研究结果表明,人类对狗的驯化发生在农业产生之前 (20),并且是在欧洲狩猎-采集文化的背景下出现的。
早前的研究显示,现代狗在进化中经历过两次大事件。第一次是驯化的起源,第二次是是近百年间的品种分化 (21)。为调查狗的种群演化历史,我们对分支A和与其亲缘关系较近的前哥伦比亚狗进行了贝叶斯Skygrid分析(Bayesian Skygrid analysis)(22)。我们发现,在MRCA至距今5000年前,狗的种群规模持续不断地增加,这可能归因于最早的驯化过程(图2)。5000至2500年前,种群数量大量减少,紧接着又是一次急速增长(图2)。这一增长轨迹和人类种群数量的变化相平行 (23),意味着狗的种群数量总是随着人类而变化的。与此相反,在这段时间内,由于农耕文化的兴起、栖息地的丧失和人为狩猎,狼的数量越来越少。
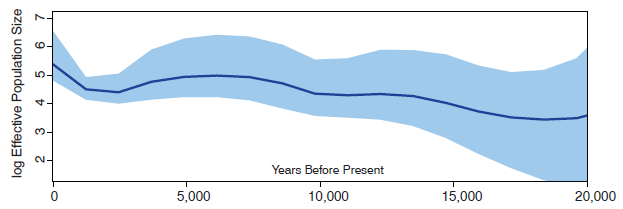
利用Bayesian Skygrid plot分析得出的狗支系A和前哥伦比亚狗的种群数量变化情况。数字代表该点距今的年数,实线代表有效种群大小的logN e中值,周围的色块表示95% HPD。
我们的发现支持了狗的线粒体起源于欧洲狼的论断。以往那些没有提出欧洲起源说的线粒体和Y染色体研究使用的现代狼、古代狼和古代狗样本数量都很有限,而且在系统进化上的统计学证据也不足 (4, 6, 24)。而我们利用全mtDNA序列所作出的现代狗系统进化树就要合理而有据得多。我们发现所有可以在现代狗身上发现的序列多样性也都能在古代(支系A、C、D)或现代(支系B)的欧洲犬科动物身上找到。分支B和瑞典、乌克兰的狼亲缘关系很近,这可能是由于在这里狗和狼存在杂交,而非这些狗起源于该地的狼,因为在这个时间,狗显然已经被驯化很久了 (8, 12, 14)。
值得注意的是,我们研究中所用的古代狗样本并没有包含中东或中国,这两个可能的起源地 (5, 6)。实际上,在这些区域,最古老的狗样本也没有早于13,000年前 (10)。不过,我们仍需要判断这些地区的史前狼和狗和四大狗支系的亲缘关系,以确定其和四大支系的联系是否比欧洲和四大支系的亲缘关系还要近,而如果如此,事实就和我们的推断不相符了。然而这同时也意味着地理分布遥远的动物具有相同的直系祖先,因此我们认为这种情况不太可能出现。不过,如果得到中东和亚洲史前狗的mtDNA数据,我们就可以更加完善这个系统进化树了。换句话说,尽管我们的系统进化树很合理,但它描绘的依然只是一些单独的基因位点。mtDNA基因组凝结很快且缺乏重组,是一个很大的优势;不过,鉴于近期狼和狗的演化分歧,不管线粒体还是核基因都经历了不完全谱系分拣(incomplete lineage sorting),这可能会混淆我们有关演化的推演。如果核基因组中有多个独立位点可用于分析,将使亲缘关系判断变得更加可靠。我们原本试图从这些史前DNA样本中使用密集平铺捕捉阵列找到这些独立的位点,但样本的保存状况实在不佳 (15)。无论如何,我们的mtDNA系统进化树表明,四个现代狗分支中,有三个和欧洲史前狼的亲缘关系很近。更进一步地,聚合时间分析显示狼和狗的演化分歧时间超过15,000年。根据这个结论,我们推断人类对狗的驯化是在末次盛冰期(Last Glacial Maximum),这时候人类主要捕食的对象是巨型动物 (25)。最初的狗可能常常从人类狩猎的残渣中获益,因此协助人类捕获猎物或保护人类免受大型掠食者的伤害。最后,我们的研究结果意味着,一些最早的狗,诸如来自比利时的Goyet dog (2) 或俄罗斯的阿尔泰狗 (13),可能和驯化失败等事件相关。如果这是真的,那么人类对狗的驯化可能就不只发生在某个特定的时间和地点,并为人们了解驯化一种大型且危险的食肉动物这一偶然的奇妙过程提供了一种新的思路。
1. G. Larson, J. Burger, Trends Genet. 29, 197–205 (2013).
2. M. Germonpré et al., J. Archaeol. Sci. 36, 473–490 (2009).
3. S. J. Olsen, J. W. Olsen, Science 197, 533–535 (1977).
4. C. Vilà et al., Science 276, 1687–1689 (1997).
5. B. M. vonHoldt et al., Nature 464, 898–902 (2010).
6. P. Savolainen, Y. P. Zhang, J. Luo, J. Lundeberg, T. Leitner, Science 298, 1610–1613 (2002).
7. G. D. Wang et al., Nat Commun 4, 1860 (2013).
8. M. Sablin, G. Khlopachev, Curr. Anthropol. 43, 795–799 (2002).
9. S. J. Crockford, Y. V. Kuzmin, J. Archaeol. Sci. 39, 2797–2801 (2012).
10. G. Larson et al., Proc. Natl. Acad. Sci. U.S.A. 109, 8878–8883 (2012).
11. H. Napierala, H.-P. Uerpmann, Int. J. Osteoarchaeol. 22, 127–137 (2012).
12. G. Nobis, Umschau 79, 610 (1979).
13. N. D. Ovodov et al., PLOS ONE 6, e22821 (2011).
14. M. Baales, Mongraphien RGZM, Mainz 38, 106 (1996).
15. Supplementary materials are available on Science Online.
16. J. A. Leonard et al., Curr. Biol. 17, 1146–1150 (2007).
17. J. A. Leonard et al., Science 298, 1613–1616 (2002).
18. B. van Asch et al., Proc. Biol. Soc. 280, 20131142 (2013).
19. H. Malmström et al., BMC Evol. Biol. 8, 71 (2008).
20. E. Axelsson et al., Nature 495, 360–364 (2013).
21. K. Lindblad-Toh et al., Nature 438, 803–819 (2005).
22. M. S. Gill et al., Mol. Biol. Evol. 30, 713–724 (2013).
23. J. A. Tennessen et al., Broad GO, Seattle GO, on behalf of the NHLBI Exome Sequencing Project, Science 337, 64–69 (2012).
24. Z. L. Ding et al., Heredity 108, 507–514 (2012).
25. J. Alroy, Science 292, 1893–1896 (2001).
人家才刚发science我就拿来翻了这样真的好吗?等等,说起来我好像也已经翻了好多公网付费才能看的文献了!(? |
|

















 发表于 2013-11-22 14:27
|
发表于 2013-11-22 14:27
| 




 发表于 2013-11-27 20:37
|
发表于 2013-11-27 20:37
| 



